
La plateforme
Présentation & Mission
SEGiCel est une plateforme de service dédiée à la communauté scientifique française, spécialisée dans l'édition du génome du nématode modèle Caenorhabditis elegans.
Grâce aux technologies CRISPR/Cas9, SEGiCel réalise des modifications ciblées : mutations ponctuelles, délétions de gènes ou insertion de séquences codantes (ex. protéines fluorescentes).
"Some strains were generated by SEGiCel (SFR Santé Lyon Est CNRS UAR 3453, Lyon, France) with the support of CNRS, Lyon 1 Université Claude Bernard, and IBiSA, within the framework of Celphedia."



Historique
Après 10 ans comme UMS 3421 du CNRS, SEGiCel a rejoint la SFR Santé Lyon-Est de Lyon 1 Université Claude Bernard en janvier 2021, tout en continuant de bénéficier du soutien du CNRS. Installée à la faculté de médecine Rockefeller, la plateforme travaille en proximité directe avec le laboratoire MeLiS.
Objectifs
SEGiCel mutualise un savoir-faire national en ingénierie du génome de C. elegans, au service de la recherche fondamentale et clinique. Elle conseille et accompagne les équipes dans leurs projets d'édition génomique.
Labellisations
2024
En novembre 2024, SEGiCel a reçu pour la première fois le label IBiSA. Le GIS IBiSA coordonne la politique nationale de labellisation et de soutien aux infrastructures nationales de recherche en biologie et santé (INBS). SEGiCel rejoint ainsi ce réseau de plus de 200 plateformes nationales.
2024
En avril 2024, SEGiCel a intégré l’infrastructure de recherche (IR) Celphedia. Sa mission est de soutenir la communauté scientifique universitaire et industrielle afin d’accélérer les découvertes en biologie et d’améliorer la recherche biomédicale. Celphedia offre un accès à de nombreux organismes modèles pour répondre aux enjeux de la biologie moderne et aux défis sociétaux. Cet accès favorise le développement d’approches multi-modèles, de la création au phénotypage et à l’archivage. L’objectif est de développer et pérenniser des méthodologies innovantes et standardisées au service de la communauté scientifique.
L'équipe
Personnels de SEGiCel

Margaux GIBERT

Marielle LIMOGES

Thomas BOULIN
Organisme modèle
Le nématode Caenorhabditis elegans
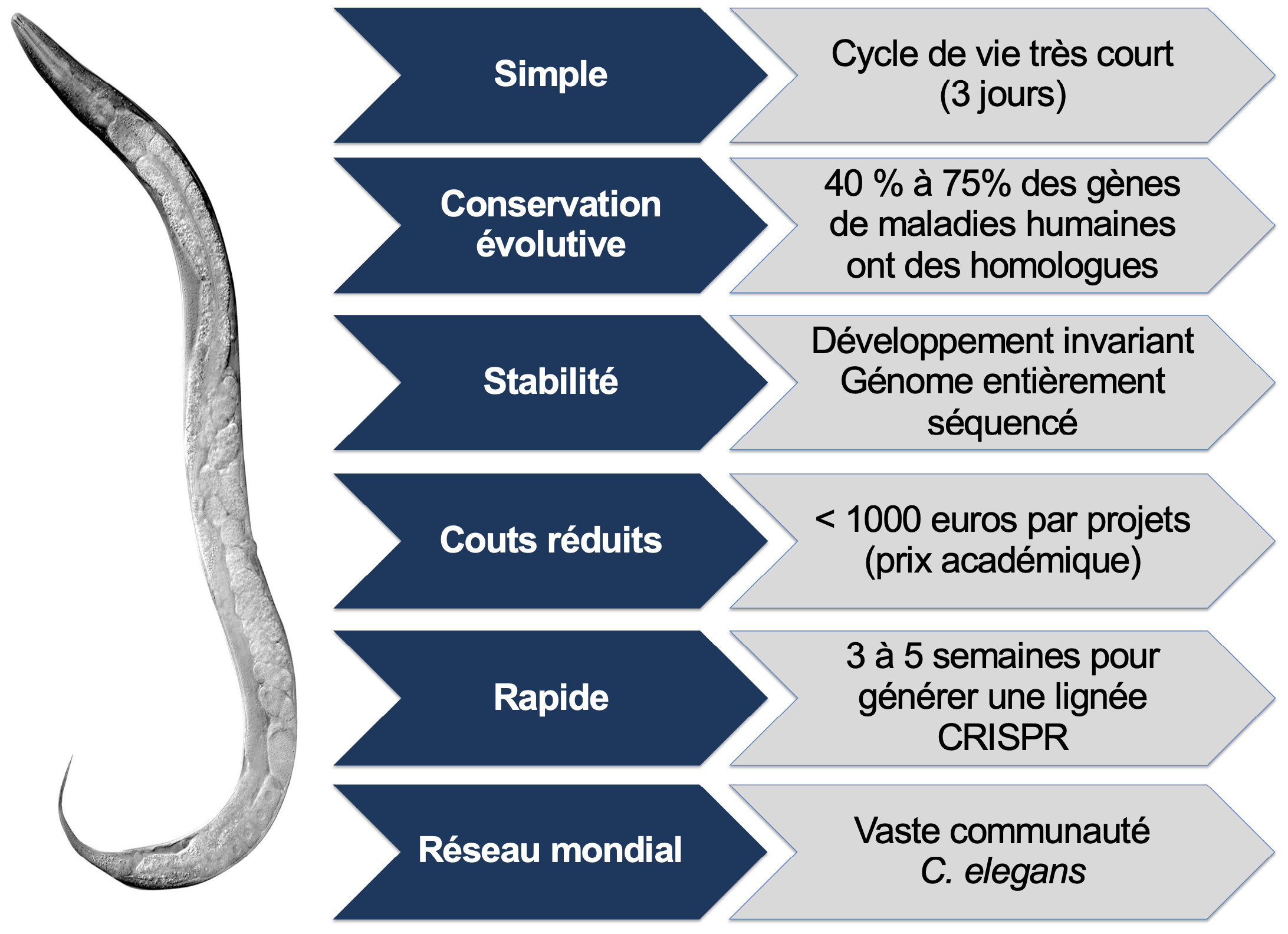
Le nématode C. elegans est un organisme modèle génétique utilisé par une grande communauté internationale pour aborder un large éventail de questions biologiques et physiopathologiques.
Grâce aux technologies CRISPR/Cas9, il est aujourd'hui possible de générer rapidement et à faible coût tout type de modification génomique : mutations ponctuelles, délétions, insertions de séquences codantes (protéines fluorescentes), ou remplacement de séquences.
Comment ça marche
Méthode de travail
1. Demande initiale
Adressez votre demande à segicel@univ-lyon1.fr en décrivant brièvement vos besoins. Si SEGiCel peut prendre en charge votre projet, nous définirons ensemble objectifs, faisabilité et délais par visio-conférence.
2. Stratégie & réalisation
Une fois la demande acceptée, nous préparons la stratégie détaillée en coordination avec vous, en tenant compte de la littérature et des contraintes expérimentales spécifiques.
3. Validation & livraison
Toutes les lignées sont validées par séquençage Sanger et accompagnées d'un rapport détaillé. SEGiCel assure également le stockage cryogénique de l'ensemble des lignées produites.
Collection
Ressources génétiques
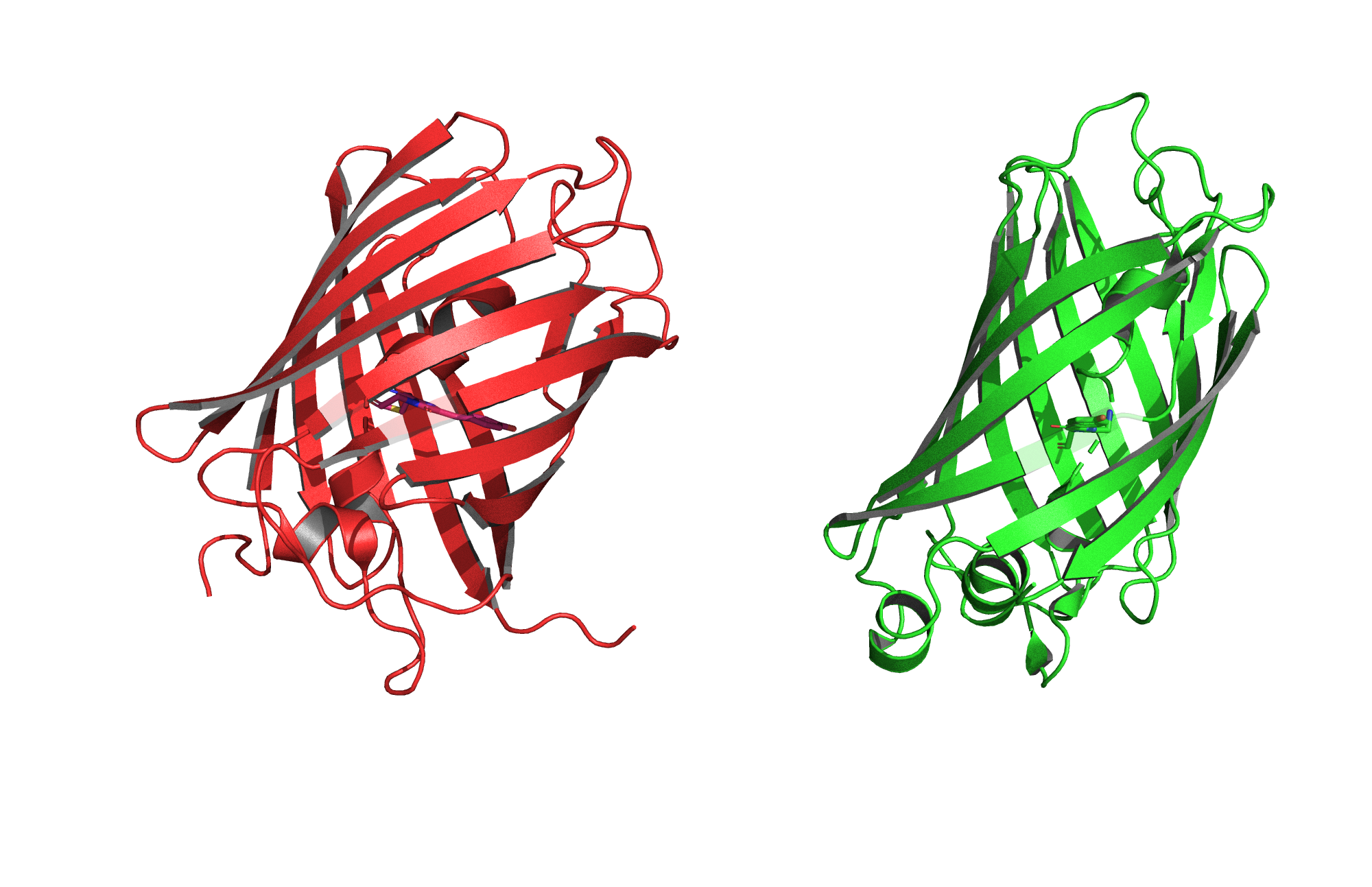
Nous disposons d'une large collection de séquences codant des protéines fluorescentes adaptées à C. elegans.
Il est également possible de nous faire parvenir des séquences spécifiques pour votre projet. Nous pouvons vous conseiller sur le choix de rapporteurs en fonction des équipements d'imagerie à votre disposition.
Rejoindre SEGiCel
Offres de Stage

Tout au long de l'année, SEGiCel accueille des stagiaires à tous niveaux, intéressés par une expérience professionnelle sur une plateforme de biotechnologie de service.
Vous apprendrez à manipuler C. elegans et les dernières techniques de biologie moléculaire.
Candidature (parcours, CV, lettre de motivation) à envoyer à Thomas BOULIN par e-mail.
Stagiaires SEGiCel
Théodore PELLETIER RIMBERT — 2e année BTS Biotechnologies, Lycée La Martinière Duchère Lyon 9e. Stage janv.–mars 2021.
Lisa ROLLET — 1ère année BTS Biotechnologies, Lycée La Martinière Duchère Lyon 9e. Stage mai–juil. 2021.
Recherche
Publications de nos utilisateurs
"Some strains were generated by SEGiCel (SFR Santé Lyon Est CNRS UAR 3453, Lyon, France) with the support of CNRS, Lyon 1 Université Claude Bernard, and IBiSA, within the framework of Celphedia."
2026
2025
2024
2023
2021
2019
Nous trouver
Contacts & Accès
Lyon 1 Université Claude Bernard
3ème étage, aile D
8 avenue Rockefeller
69373 Lyon Cedex 08

